Table of Contents
VSC-3
- Installation Sommer 2014 durch ClusterVision
- 2020 Nodes
- 2x Intel Xeon E5-2650v2, 2.6 GHz, 8 Cores
- 64 GB Ram
- 2x Infiniband QDR (40 GBit/s)
- Ölgekühlt
- 39 Storage Server
- 9 Server für Home Filesysteme
- 8 Server für paralleles Global/Scratch Filesystem
- 16 Server für parallele Bioinformatik Filesysteme
- 2 Server für GPFS
- 4 Server für Testing
Parallele Dateisysteme am VSC-3
- Home Verzeichnisse
- NFS mounts via Infiniband QDR
- BeeGFS
- Geteiltes Filesystem für alle User
- Mehrere Targets/Server (GLOBAL, BINF)
- IBM GPFS
- Kooperation mit EODC (https://www.eodc.eu)
- Remote Cluster für EODC Filesysteme
BeeGFS (1/2)
- Erstellt vom Fraunhofer Center for High Performance Computing / ThinkparQ
- Ease of Use
- Performance
- Scalability
- Aufteilung Management / Metadaten / Daten
- Management Server
- Verbindung der Nodes
- Handling von Quotas
- Metadaten Server
- Speichern Metadaten
- Root Metadaten Server
- Metadaten Mirroring möglich
- Benötigen Filesystem (Typischerweise ext4)
- Idealerweise auf schnellen SSDs
BeeGFS (2/2)
- Storage Server
- Speichern Daten
- Mirroring möglich
- Benötigen Filesystem (Oftmals xfs)
- Monitoring
- BeeGFS-Admon daemon
- Command-Line tool
- Graphisches tool (Java)
Setup am VSC-3 (1/2)
- 8x Storage Server für Global/Scratch Filesystem
- Intel Xeon E5-1620 v2, 4 Cores / 8 Threads, 3.70 GHz
- 128 GB Ram
- 48x Toshiba 2 TB SAS Disks (MG03SCA200)
- Arrangiert in vier Raid6 Arrays zu je 12 Disks
- LSI SAS2208 Controller
- 2x Samsung 240 GB SSDs (MZ7WD240)
- Raid 1 (Linux Software Raid)
- 2x Infiniband QDR Controller (40 GBit/s)
- RDMA
- Provisionierung der Betriebssysteme In-Memory
- Mittels Bright Cluster Manager
- CentOS 7.4
- Projekt-Quotas
- 384 Disks
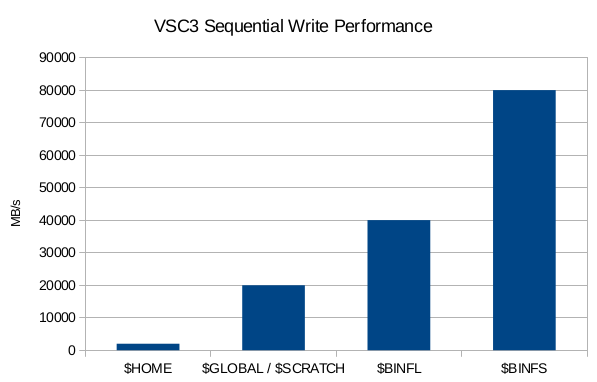
- ~0.5 PiB Space
- ~20 GiB/s Durchsatz
VSC - Fileserver
Setup am VSC-3 (2/2)
- 16x Storage Server für Bioinformatik Filesystem
- Computing auf den Knoten möglich
- 2x Intel Xeon E5-2690 v4, 14 Cores / 28 Threads, 2.60GHz
- 0.5TB - 1.5TB Ram
- 12x Seagate 8 TB SAS Disks (ST8000NM0075)
- 1 Raid6 Array an LSI SAS-3 3108 Controller
- 4x Intel DC P3600 SSDs
- 1 Raid10 (Linux Software Raid)
- 1x Infiniband QDR Controller (40 GBit/s)
- 1x Intel Omnipath Controller (100 GBit/s)
- RDMA
- Provisionierung der Betriebssysteme In-Memory
- Mittels Bright Cluster Manager
- CentOS 7.2
- Projekt-Quotas
- 192 Disks
- 64 SSDs
- ~1.1 PiB Space (100 TiB auf SSDs)
- ~80 GiB/s Durchsatz
VSC3 - Bioinformatics
Storage Performance
Erfahrungen
- Bugs?
- Ja, speziell bei neuen Features
- Support?
- Exzellent
- Bedienung?
- Relativ einfach mittels beegfs-ctl und Installations-Skripts
- Läuft problemlos auf provisionierten in-memory images
- Tipps?
- Metadaten Targets groß genug wählen
- Beim Einsatz neuer Features diese zuerst Testen ;)
- Kein automatisches rebalancing beim Hinzufügen neuer Targets (manuell möglich)
- Viel Ram
- Kein Random I/O
IBM GPFS
- General Purpose Filesystem
- Früher Multimedia Filesystem
- Linux Support seit 1999
- Storage Pools
- Cluster Export Services
- Hadoop
- Features
- Striping
- n-way Replication
- Raid (Spectrum Scale Raid)
- Fast Rebuild
- In vielen TOP500 Systemen im Einsatz
- SuperMUC / München
- Juron, Julia / Jülich
- …
GPFS @ EODC
- EODC - Earth Observation Data Center for Water Resources Monitoring
- Processing Large Volumes of EO Data
- Sentinel Satellitendaten
- Viele Petabytes
- IBM ESS (Elastic Storage Server)
- Building Blocks
- Skalierbar
- 2xESS
- 4 Server
- TS4500 Tape Library
- TSM
- Muti-Tiered (IBM HSM)
- Dateien mit ältestem zugriffsdatum kommen auf Tape
- Bei Zugriff auf Stub File wird die Datei wieder vcon Tape auf Disk geholt
- Schedules, Callbacks, Migration Control, etc…
GPFS Server @ VSC-3
- Verbindung mittels Infiniband QDR
- 2 Management Server für Remote Cluster
- Tie-Breaker Disk an dritter Maschine für Quorum
- Keine Filesysteme / Keine Disks (nur Remote FS von EODC)
- GPFS 4.2.0
- 12 Infiniband QDR Links
- 500 Client Lizenzen
- ~40GiB/s Durchsatz
Erfahrungen
- IBM typisch manchmal archaische Programme
- Aber an sich Ok
- Integration in bestehende Systeme
- mmdsh als integrierte verteilte shell
- Nettes GUI / Monitoring
Ende
- Danke für die Aufmerksamkeit